塩素化dibenzo-p-dioxin(PCDD)は毒性、催奇性が非常に高い化合物である。合成過程での副産物として、ベトナム戦争で使用された枯葉剤に含まれ、散布によって広く拡散した。現在ではPCDDを含み得る薬剤の散布は規制されているが、パルプ工業の廃水やゴミ焼却施設の排煙等にPCDDが含まれているため、日々自然界に放出され続けている。 自然環境においては多くの人為化合物は微生物による分解を受けると考えられるが、中には非常に分解性の低い化合物も存在し、自然界に放出されたこのような難分解性の有害化合物を分解・除去することは地球環境的に重要な課題である。PCDDも難分解性物質であるが、ある種の微生物により分解を受けることが示されている。PCDDの微生物分解に関する知見はリグニン資化・分解能を有するPhanerochaete chrysosporium等の真菌類によるものと細菌によるものの2つに大別できる。近年、特に真菌類によるものについては多く報告がなされ、リグニン分解系がPCDD類の分子に作用することが示されている。一方、細菌によるPCDDの分解については報告例が少なく、分解系酵素やその遺伝子に関する知見は全くないと言ってよい。しかしながら、培養が容易であることや高分解活性をもつ組換え体構築の可能性が高いことなど、細菌のdioxin分解系は応用性が高いものと考えられる。 DBF63株は、dibenzo-p-dioxin(DD)に構造が類似であるdibenzofuran(DBF)を唯一炭素源・エネルギー源として資化する菌として土壌サンプルから取得された。この菌株については、図1に示すような代謝経路が推定されている(1)。DBF63株によりDDは1-hydroxydibenzo-p-dioxinへと変換されたが、これはDBF63株のDBF代謝系酵素にdioxin骨格の核間部位に水酸基を導入する活性があることを示していた。当研究室では本菌株の他にもDBF資化菌8種、DBFに構造が類似のcarbazole資化菌を4種取得しているが、これらの中にもDBFやDDの核間部位に水酸基を導入する能力があるものがあり、この様な酸素添加能を有する細菌は希な存在ではなく、普遍的に存在しているものと考えられる。そこで本研究では細菌によるDDの分解に関与する酵素遺伝子の解明、細菌による効率の良いDD分解系の構築を目的とし、分解系モデルとしてDBF63株のDBF分解系を用いて基礎的研究を行った。  Fig.1 Degradation of dibenzofuran(DBF)and fluorene and co-metabolism of dibenzo-p-dioxin (DD)by Strain DBF631DBF63株の再分類 Fig.1 Degradation of dibenzofuran(DBF)and fluorene and co-metabolism of dibenzo-p-dioxin (DD)by Strain DBF631DBF63株の再分類 DBF63株は当初、定常期の観察からグラム陽性球菌とされ、更に生理学的性質からStaphylococcus属細菌と同定されていた。しかしながら、本菌株のgenomeを用いたDNA操作の過程で、DBF63株genomeのG+C含量が70%を超える高いものであることが示され、Staphylococcus属細菌のgenomeの一般的なG+C含量値(約40%)とは大きくかけ離れていることが示された。そこで本菌株がArthrobacter属細菌やRhodococcus属細菌など培養後期には球形に近くなるグラム陽性桿菌の一種である可能性も考慮し、16S rRNA遺伝子の部分配列を決定することで菌株の再同定を行った。その結果、本菌株の16S rRNA遺伝子は、塩基配列の決定された1.15kbの範囲でTerrabacter属細菌のtypestrainであるT.tumescensと95.6%の相同性が見られた。このT.tumescensとDBF63株では菌学的性質に多くの一致点、類似点が見いだされるため、本菌株はTerrabacter属細菌、またはその近縁種であると示された。 2Dibenzofuran分解に関与するメタ開裂酵素遺伝子の取得と解析 DBF63株はcatechol化合物に対して非常に強いメタ開裂活性を有することが示されていたため、まず、DBF分解系に関与する遺伝子の取得の足がかりとしてメタ開裂酵素遺伝子のショットガンクローニングを行なった。スクリーニングに用いたcatechol化合物としては、DBF中間代謝物と考えられる2,2’,3-trihydroxybiphenyl(THB)の代替基質として2,3-dihydroxybiphenyl(DHB)を用いた。大腸菌MV1184株とpUC119を用いたgenomic libraryから、DHBに対してメタ開裂活性を示し、メタ開裂物質由来のコロニーの黄変が観察された形質転換体を選抜した。この結果、3kb BamHl断片をもつpLM1、4kb Pstl断片をもつpLM21、8kb Sphl断片をもつpKN1の3種のクローンが得られた。制限酵素地図とSouthern hybridizationの結果からpLM1とpLM21にコードされているメタ開裂酵素遺伝子は同一のものであることが示された。 pLM1、pLM21上のメタ開裂酵素遺伝子は大腸菌において高い酵素活性を発現させ、DHBに対する活性は3-methyl-catecholに対する活性の10倍以上であった。ORFの上流には大腸菌内で機能しうるプロモーター様配列が存在していた。一方、pKN1上のメタ開裂酵素遺伝子から発現させた酵素活性はpLM1にコードされているのものに比較して低く、DHBに対する活性と3-methylcatecholに対する活性に大差はなく、プロモーター様配列は存在していなかった。この活性評価の結果から、biphenyl骨格のcatechol化合物であるTHBに対してはpLM1上にコードされたメタ開裂酵素の方が強い活性を持つことが予想された。 この両者の塩基配列決定の結果、pLM1のメタ開裂酵素遺伝子(ORFL1)はcatechol2,3-dioxygenase familyに、pKN1の遺伝子(ORFK1)はprotocatechuate 4,5-dioxygenase familyに属するものであることが示された。また、各々の遺伝子の下流にはメタ開裂産物に対する加水分解酵素遺伝子(ORFL2,ORFK2)の存在が示された。 3メタ開裂酵素遺伝子の周辺領域の遺伝子解析 前章において述べたようにORFL1の遺伝子産物がDHBに対し非常に高いメタ開裂活性を示し、DHBと3-methylcatecholに対する基質特異性に差があったことから、THBのメタ開裂反応にはORFL1の遺伝子産物が関与している可能性が高いものと考えられた。そこで、ORFL1L2の周辺領域の遺伝子解析を行うために、大腸菌MV1184株とcharomid 9-28から構築したコスミドライブラリーを構築し、pLM21の4kb Pstl断片の周辺領域を30kbにわたって取得した。これらのコスミドクローンではDBFやSAに対する変換能は検出されなかった。 この周辺領域を両方向に計8.6kbにわたってDNA塩基配列を決定し、ORF解析を行った(図2)。 ORFL3はhomology解析の結果、Alcaligenes eutrophus JMP134の2,4-dichlorophenol hydroxylase遺伝子(tfdB)と49%、Pseudomonas sp.ECT1001のphenol hydroxylase遺伝子(pheA)と45%、Streptomyces glaucescensのhydroxylase遺伝子(tcmG)と39%のアミノ酸残基が一致していたことから、芳香族化合物のヒドロキシラーゼの遺伝子である可能性が示された。また、この推定アミノ酸配列ではglycine-richな 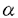  構造をとるNAD結合部位、VFVAGDというFAD結合部位等が保存されていた。しかしながらORFL3はpUC vectorのlac promoterの制御下では発現させることができなかった。 構造をとるNAD結合部位、VFVAGDというFAD結合部位等が保存されていた。しかしながらORFL3はpUC vectorのlac promoterの制御下では発現させることができなかった。 またORFL3のflanking regionにはBurkholderia cepaciaのIS401にhomologyの高いDNA領域が存在していた。Southern hybridizationの結果から、このIS様配列にhomologyの高いDNA領域が他にも存在していることが示された。このIS様配列の機能や転移活性に関する解析は行っていないが、genome再編などに関与している可能性が考えられる。 ORFL1の上流領域には芳香族化合物の代謝に関与すると考えられる有意な塩基配列は検出されなかった。 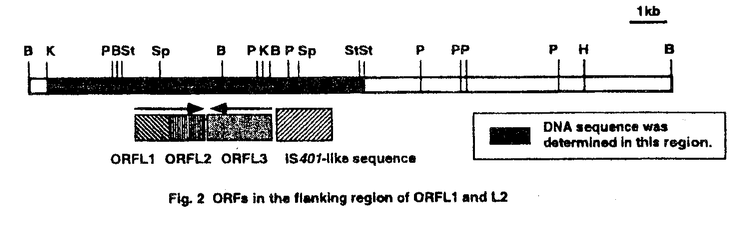 Fig.2 ORFs in the flanking region of ORFL1 and L24.DBF資化能欠損株の取得と解析 Fig.2 ORFs in the flanking region of ORFL1 and L24.DBF資化能欠損株の取得と解析 DBF63株を栄養培地上で継体培養し、DHBに対するメタ開裂酵素活性の弱い株(DBF63W株)を取得した。この株は野生株と異なりDBFやfluoreneに対する資化能、分解能が欠損していることが示された。Southern hybridizationにより、ORFK1K2は両株で、ORFL1L2は野生株のみで保持されていることが示され、この結果からもORFL1L2がDBF63株のDBF分解に関与していると考えられた。 5遺伝子産物の活性発現とDD、DBFの分解 ORFL1、ORFL2のそれぞれ、または双方を大腸菌内でlac promoterの制御下で発現させ、SDS-PAGEで解析したところ、可溶性画分にそれぞれ約34kDa、30kDaのpolypeptideのbandが観察された。また、両酵素を共に発現させた大腸菌の菌体を用いた休止菌体反応では、DHBが安息香酸に変換され、両酵素が活性型で発現していることが示された。 最近carbazole資化菌Pseudomonas sp.CA10株からクローニングされたcarbazole dioxygenase(CarA)はcarbazoleのみならず、DBFやDDに対してもDBF63株と同様に核間へのdioxygenation活性を有しており、DBF、DDをTHB、2,2’,3-trihydroxydiphenyl ether(THDE)へと変換する。そこでこの遺伝子とORFL1L2を共存させた大腸菌を用いて、ORFL1L2の遺伝子産物の活性評価を行った。その結果、ORFL1L2産物によってTHBはSAまで変換されることが確認され、THDEは分解を受けて消失することが確認された。THDEはORFL1産物によりメタ開裂を受けた後、大腸菌由来のesteraseにより更に分解された可能性も考えられる。また、THDEが分解されて生成すると考えられるcatecholは更にメタ開裂を受けた可能性が高く、最終的な分解産物を同定するには至っていない。 ORFL3の役割はDBFまたはSAに対するhydroxylaseである可能性が考えられた。この遺伝子はpUC vectorのlac promoterの制御下では発現が確認されなかったが、これはおそらくORFL3が大腸菌内で効率よく発現するためのribosome binding site(RBS)が存在していなかったことによるものと考えられた。そこで遺伝子の直前に強力なRBSを導入し、強制発現させた上で活性や機能を評価することにした。ORFL3の推定開始コドン部位にsite-directed mutagenesisによってNdetl切断部位を導入し、ORFL3をpET26b(+)のT7 promoterの下流に連結し大量発現させた。生合成されたタンパクは培養条件を変化させても不溶性画分として検出され、inclusion bodyを形成しているものと推定された。そこで、ORFL3をRBSと共に低コピーplasmid pSTV29に再クローン化して発現実験を行ったところ、生産物は可溶性画分に63kDaのサイズで検出され、これは計算値63.2kDaとよく一致した。この形質転換体の2,4-dichlorophenolやphenol、SA、DBF等に対する活性を休止菌体反応で評価したが活性は認められなかった。ある種のphenol hydroxylaseの遺伝子は大腸菌内で発現させても活性が見られない場合が知られているため、活性評価のためには、大腸菌ではなくPseudomonas属細菌など他の宿主を用いることを検討する必要がある。 Ref1)Monna,L.,Omori,T.,and Kodama,T.(1993)Microbial degradation of dibenzofuran,fluorene,and dibenzo-p-dioxin by Staphylococcus auriculans DBF63.Appl.Environ.Microbiol.,59:285-289. |